Journées du Protéome et Peptidome Verts les 1er et 2 juin 2026 à l'Université de Grenoble Alpes
Journées PROTÉOME et PEPTIDOME VERTS des 1er et 2 juin 2026
Bâtiment IMAG, Université Grenoble Alpes, 150 place du Torrent, 38400 Saint-Martin-d’Hères
Bâtiment IMAG, Université Grenoble Alpes, 150 place du Torrent, 38400 Saint-Martin-d’Hères
La transition agroécologique est un enjeu majeur pour une agriculture plus durable et plus respectueuse de l’environnement. Pour y contribuer, il est essentiel de mieux comprendre le fonctionnement des agroécosystèmes, grâce à des recherches interdisciplinaires prenant en compte la diversité génétique des organismes vivants ainsi que leurs interactions multiples en condition in situ, comme par exemple les interactions entre plantes voisines ou entre les plantes et le sol en plein champ. Ces recherches sont généralement basées sur l’intégration de données multi-omiques acquises sur un très grand nombre d’échantillons. Dans ce contexte, la protéomique devient un des outils de phénotypage moléculaire offrant de nouvelles opportunités en agroécologie.
Au terme d’un processus d’élargissement visant à intégrer de nouvelles expertises, l’infrastructure nationale en protéomique ProFI intègre la plateforme PAPPSO au 1er janvier 2026.
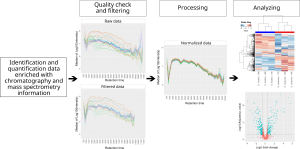
MCQR is an R package R package for the in-depth exploration, processing, and analysis of quantitative proteomics data generated from either data-dependent or data-independent acquisition methods. It has been recently accepted for publication in Journal of Proteome research
Les plateformes omiques végétales du plateau de Saclay organisent les 23 et 24 juin 2025 un colloque dédié aux approches qu’elles développent : “Les Journées des Omiques Végétales”.